《哨兵1SAR空间数据包协议数据单元》文档对数据包的结构进行了详细描述,并提供了用户数据的格式和解码算法。
原文链接: 哨兵1SAR空间数据包协议数据单元文档英文版

同系列中的其他文章篇链接:
哨兵1SAR空间数据包协议数据单元文档(一)
哨兵1SAR空间数据包协议数据单元文档(二)
哨兵1SAR空间数据包协议数据单元文档(三)
哨兵1SAR空间数据包协议数据单元文档(四)
哨兵1SAR空间数据包协议数据单元文档(五)
哨兵1SAR空间数据包协议数据单元文档(六)
今天介绍的内容如下:


哨兵1SAR空间数据包协议数据单元文档(七)
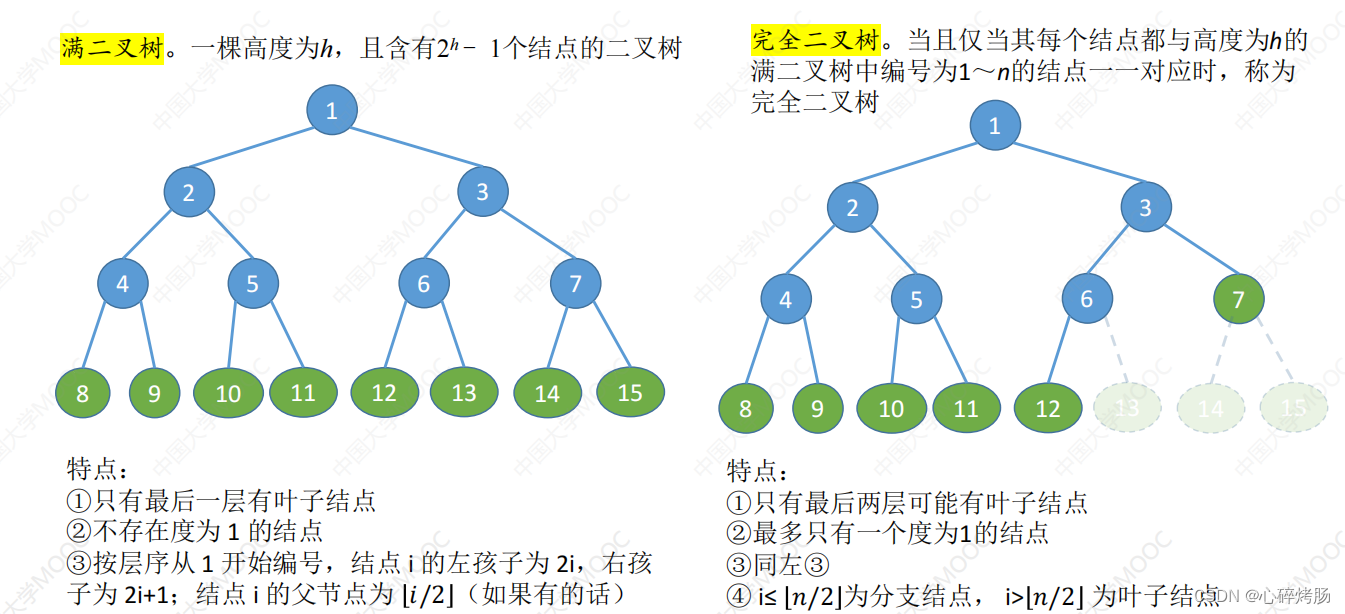
4 用户数据字段解码
4.1 概述
4.1.1 用于解码的符号
• NRL:归一化重建水平(Normalized Reconstruction Level),用于表示量化雷达样本的重建电平,归一化到标准差为1。
• SF:西格玛因子(Sigma Factor),用于将归一化的样本值上缩放至原始功率水平。
• THIDX:阈值索引(Threshold Index),用于确定解码过程中使用的特定阈值表。
• BRC:比特率代码(Bit Rate Code),表示FDBAQ压缩模式下的比特率。(可以理解成压缩比)
• HCode:霍夫曼码(Huffman Code),包括符号位和霍夫曼编码的幅度。
• MCode:幅度代码(Magnitude Code),表示量化后的幅度值。
• MValue:幅度值(Magnitude Value),实际的幅度大小。
• SCode:样本代码(Sample Code),用于表示解码后的样本值。
• SValue:样本值(Sample Value),解码得到的最终样本值。
• NQ:样本对数(Number of Quads),数据包中复数样本的数量。
• NB:BAQ块数(Number of BAQ Blocks),表示数据包中BAQ压缩块的数量。
• NW:(16位)字数量(Number of Words),表示数据部分中16位字的总数。
• Sign:符号位,表示样本是正数还是负数。
• b:BAQ块索引(BAQ Block Index),用于在解码过程中标识特定的BAQ块。
• k:量化级别数(Number of Quantisation Levels),在量化过程中使用的级别数量。
4.1.2 解码原理
解码用户数据字段中的压缩雷达样本(I或Q分量)的原理在图4-1中展示。
对于“A旁路”或“仅解采样”用户数据(格式类型A和B),不需要特定的雷达样本值重建,因为样本的幅度代码(MCode)与幅度值(MValue)相同。
图4-1: 压缩代码的解码原理
• FDBAQ解码(格式类型D)
• BAQ解码(格式类型C)
• 旁路和仅解采样(格式类型A & B)

4.2 数据格式类型A和B的解码(“Bypass"或"Decimation Only”)
数据格式类型A和B的描述见表4.2-1。

每个通道的16位字的数目NW是相同的,由以下公式给出:

10位样本代码(SCode)由1位符号位后跟9位幅度代码(MCode)组成。
在IE、IO、QE、QO通道中每个样本值的重建如下:

例如:
𝑆𝐶𝑜𝑑𝑒(二进制)=10 1011 1100 (二进制)
𝑆𝐶𝑜𝑑𝑒(无符号)=𝑀𝐶𝑜𝑑𝑒=188
𝑆𝑖𝑔𝑛=1(1位符号位)
𝑆𝑉𝑎𝑙𝑢𝑒=−188
样本对齐: 在PRI范围内的复数样本序列将通过以下方式排列4个通道(IE、IO、QE、QO)的样本值来获得:

4.3 数据格式类型C的解码(“解采样 + BAQ”)
数据格式类型C与4.2节中描述的类似。然而,由于BAQ压缩,SCodes更短。
此外,在通道数据部分,BAQ编码的数据被组织在BAQ块中。每个BAQ块都有一个与之关联的8位阈值索引,包含在QE通道数据中。
格式类型C数据的排列方式如表4.3-1所示。


BAQ块的数量NB是:

IE、IO和QO通道的16位字的数量NW是:

QE通道的16位字的数量NW与其它通道不同,因为它包括每个BAQ块的8位阈值索引:

图4-2: 数据格式类型C的解码

图4-3: 每个BAQ块b的SCode提取
每个BAQ块包含128个SCodes,除了最后一个BAQ块,它包含的SCodes数量为NQ-128*(NB-1)

图4-4: 从SCode重建样本值

图4-4中的样本值重建可以按照简单重建或标准重建执行,这取决于BAQ块b的阈值索引THIDX的值。所有BAQ模式的详细样本重建法则定义如下:

A3THIDX、A4THIDX和A5THIDX这些值取决于THIDX的数值,它们在附录的第5.2.1节中定义。
NRL和SF的值应在附录第5.2.2节中的相应表格里给出。
示例1(标准重建):
• BAQ模式:3位(BAQMOD=3)
• 阈值索引 THIDX:130
• 样本代码 SCode:6
• SCode 二进制表示:110
• 符号 Sign:1(表示负数)
• 幅度码 MCode:2
• 归一化重建级别 NRL:1.344
• Sigma 因子 SF:100.58
将给定的值代入公式得到: SValue=(−1)^1×1.344×100.58=−135.1795
示例2(简单重建):
• BAQ模式:5位(BAQMOD=5)
• 阈值索引THIDX:9
• 样本代码 SCode:27
• SCode 二进制表示:11011
• 符号 Sign:1(表示负数)
• 幅度码 MCode:11
代入公式SValue=(−1)1*11=-11
示例3(简单重建):
• BAQ模式:5位(BAQMOD=5)
• 阈值索引 THIDX:9
• 样本代码 SCode:15
• SCode 二进制表示:01111
• 符号 Sign:0((-1)0表示正数)
• 幅度码 MCode:15
代入公式SValue=(-1)^0* (A5THIDX=9)=16.3800
样本对齐:
在PRI(脉冲重复间隔)范围内的复数样本序列将通过以下方式排列4个通道(IE、IO、QE、QO)的样本值来获得:

4.4 数据格式类型D的解码
类型D的数据格式也像4.3节中描述的那样,以BAQ块结构化。
然而,类型D数据是霍夫曼编码的,这在每个BAQ块中引入了不可预测的变长HCode。
类型D数据的排列在表4.4-1中展示。HCode的长度和数量NW在表中用“问号”表示,因为它们是不可预测的,必须在霍夫曼解码过程中确定(见图4-6、图4-7、图4-8、图4-9、图4-10、图4-11)。
表4.4-1如下图所示:


所提出的空间数据包用户数据字段的解码方案在图4-5中展示,HCode的解码过程在图4-6中展示,并且适用的霍夫曼解码树在图4-7至图4-11中展示。


每个BAQ块(NB个块)包含128个HCodes,除了最后一个BAQ块,它包含𝑁𝑄-128×(𝑁𝐵-1)个HCodes。
适用于BRC的五个值的霍夫曼二进制解码树在图4-7到图4-11中展示。
可以通过逐步检查HCode的每个比特位(不包括符号位),并相应地遵循自上而下的二进制霍夫曼解码树中的相同比特模式,直到检测到相关的MCode,从而恢复出MCode。
检测到MCode表示一个HCode模式的结束。紧接着的比特位则表示下一个HCode模式的符号位,以此类推……





样本值从SCode(符号位和MCode)的重建遵循与第4.3节图4-4所示的类似流程。
针对FDBAQ模式下每种比特率的详细样本重建法则(由BRC值指示)定义如下:

B0THIDX、B1THIDX、B2THIDX、B3THIDX和B4THIDX这些值取决于THIDX的值,并且在附录的第5.2.1节中定义。
NRL和SF的值应在附录第5.2.2节中的相应表格里给出。
示例1(标准重建):
• BRC(比特率控制值)= 2, k=7
• THIDX(阈值索引)= 239
• HCode(霍夫曼码,二进制)= 011 1110
• 符号位(Sign)= 0
• 去除符号位的HCode(二进制)= 11 1110
• MCode(量化码)= 5
• NRL(归一化重建等级)= 2.5084
• SF(Sigma因子)= 237.19
• SValue(样本值)= ((-1)^Sign) * NRL * SF = 594.96
示例2(简单重建):
• BRC(比特率控制值)= 3, k=10
• THIDX(阈值索引)= 3
• HCode(霍夫曼码,二进制)= 1 1111 1111
• 符号位(Sign)= 1
• 去除符号位的HCode(二进制)= 1111 1111
• MCode(量化码)= 9
• SValue(样本值)= ((-1)^Sign) * 9 = -9
示例3(简单重建):
• BRC(比特率控制值)= 3, k=10
• THIDX(阈值索引)= 5
• HCode(霍夫曼码,二进制)= 1 1111 1111
• 符号位(Sign)= 1
• 去除符号位的HCode(二进制)= 1111 1111
• MCode(量化码)= 9
• SValue(样本值)= ((-1)^Sign) * 9.4800 = -9.4800
样本对齐:
在PRI(脉冲重复间隔)范围内的复数样本序列将通过以下方式排列4个通道(IE、IO、QE、QO)的样本值来获得:

5 附录
5.1 衰减后样本数量计算的支持表格
存在两个查找表,用于计算衰减后(或在空间数据包中)的复数样本数量:
• 一个查找表是“D”值表,它将根据“C”值(见3.2.5.12节)和滤波器编号(见3.2.5.4节)来索引。
• 另一个查找表是“滤波器输出偏移”表,它将根据滤波器编号来索引。
这些表格在文档的表5.1-1和表5.1-2中展示。
滤波器编号等同于头部参数“RGDECcode”(见3.2.5.4节)。


注意,滤波器及其对应的“滤波器输出偏移”值是SES雷达数据库中的可配置参数。
信息说明:每个滤波器的“滤波器输出偏移”值取决于滤波器的长度NF:

(每个滤波器的NF值在第3.2.5.4节给出)
5.2 样本重建表格
5.2.1 简单重建方法表格
对于特定的THIDX值,将应用简单重建。简单重建在第4.3节和4.4节中的重建法则部分有描述。简单重建法则需要额外的参数A或B,这些参数为不同压缩模式下相关THIDX值定义,在以下表5.2-1中给出。

5.2.2 标准重建方法表格
对于不适用简单重建方案的压缩雷达样本,将通过标准重建方案进行解压缩。标准重建方案需要归一化重建等级(Normalized Reconstruction Levels,简称NRL)和Sigma因子(Sigma Factors,简称SF)的值。这些值在以下小节中定义。
5.2.2.1 归一化重建等级(NRL)
选定的NRL值代表重建样本值归一化到标准偏差等于1。使用表5.2-3中的Sigma因子将归一化样本值上移到SAR原始数据中测量到的真实标准偏差。
NRL表格列在表5.2-2中,将根据量化雷达样本的幅度码(Magnitude Code,简称Mcode)和BAQ模式(见3.2.5.1)进行索引:
• 在BAQ压缩情况下:
o 由BAQMODCode = 3、4或5(分别表示3位、4位或5位BAQ)指示。
• 在FDBAQ压缩情况下(由BAQMODCode = 12、13或14指示):
o 由IE通道数据的用户数据字段中的BRC值决定。

5.2.2.2 Sigma因子(SF)
Sigma因子用于将归一化到标准偏差等于1的样本值上移到BAQ块中的原始功率水平。Sigma因子列在表5.2-3中,将根据用户数据字段的QE通道数据中的THIDX进行索引。

5.3 校准信号采集时序
校准信号的采集时序基于固定的时序,这只依赖于数据采集中选定的发射脉冲的长度TPL。它不依赖于命令参数SWST和SWL。
时序如图5-1所示。

在校准PRI(脉冲重复间隔)中,CWL(校准波束长度)的值将由仪器自动选择为:

其中,CWL_Delta是仪器雷达数据库[IRD 07]中定义的任务参数。

t26和t9也是仪器雷达数据库[IRD 07]中定义的任务参数。

可以看出,tguard2始终是一个固定值,由任务参数定义,与发射脉冲长度无关。
需要注意的是,发射脉冲信号在其生成时不会被TxM模块采样,因为发射信号需要通过仪器信号路径(例如天线的路径)传播后才能被接收、数字化和在RxM模块中处理。因此,tguard2被应用以覆盖这一信号延迟。
数据包中捕获的校准样本数量可以表示为:


数字滤波器抑制了采集采样窗口中的FIR(有限脉冲响应)滤波器瞬态。数据包中捕获的数据对应于在采集采样窗口开始后采样的𝑡suppr数据。

5.4 EFE和TGU温度校准
5.4.1 TGU温度校准

5.4.2 EFE温度校准